Model info
| Transcription factor | Fosb | ||||||||
| Model | FOSB_MOUSE.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 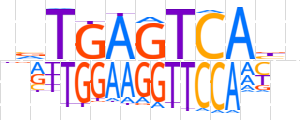 | ||||||||
| LOGO (reverse complement) |  | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 11 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | nvTGAGTCAbn | ||||||||
| Best auROC (human) | 0.97 | ||||||||
| Best auROC (mouse) | 0.919 | ||||||||
| Peak sets in benchmark (human) | 2 | ||||||||
| Peak sets in benchmark (mouse) | 27 | ||||||||
| Aligned words | 523 | ||||||||
| TF family | Fos-related factors {1.1.2} | ||||||||
| TF subfamily | Fos factors {1.1.2.1} | ||||||||
| MGI | MGI:95575 | ||||||||
| EntrezGene | GeneID:14282 (SSTAR profile) | ||||||||
| UniProt ID | FOSB_MOUSE | ||||||||
| UniProt AC | P13346 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Fosb expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 70.0 | 17.0 | 55.0 | 8.0 | 60.0 | 6.0 | 14.0 | 5.0 | 54.0 | 35.0 | 17.0 | 8.0 | 22.0 | 36.0 | 79.0 | 7.0 |
| 02 | 7.0 | 0.0 | 2.0 | 197.0 | 1.0 | 0.0 | 0.0 | 93.0 | 5.0 | 1.0 | 1.0 | 158.0 | 1.0 | 1.0 | 0.0 | 26.0 |
| 03 | 3.0 | 2.0 | 8.0 | 1.0 | 0.0 | 0.0 | 0.0 | 2.0 | 2.0 | 1.0 | 0.0 | 0.0 | 4.0 | 7.0 | 425.0 | 38.0 |
| 04 | 8.0 | 0.0 | 0.0 | 1.0 | 3.0 | 1.0 | 0.0 | 6.0 | 408.0 | 9.0 | 0.0 | 16.0 | 35.0 | 0.0 | 0.0 | 6.0 |
| 05 | 62.0 | 0.0 | 392.0 | 0.0 | 2.0 | 0.0 | 7.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 3.0 | 0.0 | 26.0 | 0.0 |
| 06 | 1.0 | 1.0 | 2.0 | 63.0 | 0.0 | 0.0 | 0.0 | 0.0 | 4.0 | 2.0 | 6.0 | 413.0 | 0.0 | 1.0 | 0.0 | 0.0 |
| 07 | 1.0 | 4.0 | 0.0 | 0.0 | 0.0 | 3.0 | 1.0 | 0.0 | 0.0 | 7.0 | 1.0 | 0.0 | 25.0 | 449.0 | 0.0 | 2.0 |
| 08 | 24.0 | 0.0 | 1.0 | 1.0 | 453.0 | 4.0 | 1.0 | 5.0 | 2.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 2.0 |
| 09 | 33.0 | 210.0 | 76.0 | 160.0 | 0.0 | 0.0 | 1.0 | 3.0 | 0.0 | 2.0 | 0.0 | 0.0 | 1.0 | 2.0 | 1.0 | 4.0 |
| 10 | 6.0 | 13.0 | 5.0 | 10.0 | 75.0 | 57.0 | 14.0 | 68.0 | 27.0 | 21.0 | 12.0 | 18.0 | 36.0 | 55.0 | 30.0 | 46.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.814 | -0.585 | 0.574 | -1.314 | 0.66 | -1.586 | -0.774 | -1.756 | 0.556 | 0.126 | -0.585 | -1.314 | -0.332 | 0.154 | 0.934 | -1.441 |
| 02 | -1.441 | -4.388 | -2.57 | 1.845 | -3.113 | -4.388 | -4.388 | 1.096 | -1.756 | -3.113 | -3.113 | 1.625 | -3.113 | -3.113 | -4.388 | -0.168 |
| 03 | -2.22 | -2.57 | -1.314 | -3.113 | -4.388 | -4.388 | -4.388 | -2.57 | -2.57 | -3.113 | -4.388 | -4.388 | -1.962 | -1.441 | 2.613 | 0.207 |
| 04 | -1.314 | -4.388 | -4.388 | -3.113 | -2.22 | -3.113 | -4.388 | -1.586 | 2.572 | -1.201 | -4.388 | -0.644 | 0.126 | -4.388 | -4.388 | -1.586 |
| 05 | 0.693 | -4.388 | 2.532 | -4.388 | -2.57 | -4.388 | -1.441 | -3.113 | -4.388 | -4.388 | -4.388 | -4.388 | -2.22 | -4.388 | -0.168 | -4.388 |
| 06 | -3.113 | -3.113 | -2.57 | 0.709 | -4.388 | -4.388 | -4.388 | -4.388 | -1.962 | -2.57 | -1.586 | 2.584 | -4.388 | -3.113 | -4.388 | -4.388 |
| 07 | -3.113 | -1.962 | -4.388 | -4.388 | -4.388 | -2.22 | -3.113 | -4.388 | -4.388 | -1.441 | -3.113 | -4.388 | -0.206 | 2.667 | -4.388 | -2.57 |
| 08 | -0.246 | -4.388 | -3.113 | -3.113 | 2.676 | -1.962 | -3.113 | -1.756 | -2.57 | -4.388 | -4.388 | -4.388 | -4.388 | -4.388 | -4.388 | -2.57 |
| 09 | 0.068 | 1.909 | 0.895 | 1.637 | -4.388 | -4.388 | -3.113 | -2.22 | -4.388 | -2.57 | -4.388 | -4.388 | -3.113 | -2.57 | -3.113 | -1.962 |
| 10 | -1.586 | -0.846 | -1.756 | -1.1 | 0.882 | 0.609 | -0.774 | 0.785 | -0.13 | -0.378 | -0.924 | -0.529 | 0.154 | 0.574 | -0.026 | 0.397 |