Model info
| Transcription factor | Nfkb1 | ||||||||
| Model | NFKB1_MOUSE.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 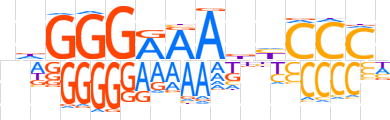 | ||||||||
| LOGO (reverse complement) |  | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 14 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | ndGGGRAAbhCCCh | ||||||||
| Best auROC (human) | 0.787 | ||||||||
| Best auROC (mouse) | 0.965 | ||||||||
| Peak sets in benchmark (human) | 7 | ||||||||
| Peak sets in benchmark (mouse) | 16 | ||||||||
| Aligned words | 528 | ||||||||
| TF family | NF-kappaB-related factors {6.1.1} | ||||||||
| TF subfamily | NF-kappaB p50 subunit-like factors {6.1.1.1} | ||||||||
| MGI | MGI:97312 | ||||||||
| EntrezGene | GeneID:18033 (SSTAR profile) | ||||||||
| UniProt ID | NFKB1_MOUSE | ||||||||
| UniProt AC | P25799 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Nfkb1 expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 73.0 | 7.0 | 31.0 | 52.0 | 64.0 | 13.0 | 12.0 | 43.0 | 46.0 | 8.0 | 17.0 | 26.0 | 37.0 | 12.0 | 42.0 | 17.0 |
| 02 | 7.0 | 1.0 | 211.0 | 1.0 | 5.0 | 2.0 | 28.0 | 5.0 | 2.0 | 0.0 | 99.0 | 1.0 | 3.0 | 3.0 | 129.0 | 3.0 |
| 03 | 1.0 | 0.0 | 16.0 | 0.0 | 3.0 | 0.0 | 3.0 | 0.0 | 26.0 | 2.0 | 438.0 | 1.0 | 1.0 | 1.0 | 8.0 | 0.0 |
| 04 | 1.0 | 0.0 | 29.0 | 1.0 | 0.0 | 0.0 | 2.0 | 1.0 | 4.0 | 1.0 | 455.0 | 5.0 | 0.0 | 0.0 | 1.0 | 0.0 |
| 05 | 4.0 | 0.0 | 1.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 343.0 | 3.0 | 130.0 | 11.0 | 6.0 | 0.0 | 1.0 | 0.0 |
| 06 | 300.0 | 15.0 | 33.0 | 6.0 | 2.0 | 0.0 | 1.0 | 0.0 | 119.0 | 6.0 | 7.0 | 0.0 | 1.0 | 1.0 | 0.0 | 9.0 |
| 07 | 396.0 | 1.0 | 25.0 | 0.0 | 22.0 | 0.0 | 0.0 | 0.0 | 40.0 | 1.0 | 0.0 | 0.0 | 15.0 | 0.0 | 0.0 | 0.0 |
| 08 | 64.0 | 69.0 | 139.0 | 201.0 | 0.0 | 0.0 | 2.0 | 0.0 | 0.0 | 1.0 | 0.0 | 24.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 09 | 20.0 | 22.0 | 3.0 | 19.0 | 3.0 | 29.0 | 0.0 | 38.0 | 22.0 | 44.0 | 10.0 | 65.0 | 19.0 | 80.0 | 9.0 | 117.0 |
| 10 | 7.0 | 46.0 | 10.0 | 1.0 | 15.0 | 158.0 | 2.0 | 0.0 | 1.0 | 16.0 | 5.0 | 0.0 | 13.0 | 221.0 | 4.0 | 1.0 |
| 11 | 0.0 | 34.0 | 1.0 | 1.0 | 24.0 | 409.0 | 3.0 | 5.0 | 9.0 | 2.0 | 0.0 | 10.0 | 0.0 | 1.0 | 0.0 | 1.0 |
| 12 | 2.0 | 21.0 | 8.0 | 2.0 | 27.0 | 404.0 | 6.0 | 9.0 | 1.0 | 0.0 | 3.0 | 0.0 | 1.0 | 5.0 | 3.0 | 8.0 |
| 13 | 12.0 | 7.0 | 11.0 | 1.0 | 143.0 | 91.0 | 43.0 | 153.0 | 7.0 | 5.0 | 6.0 | 2.0 | 11.0 | 0.0 | 3.0 | 5.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.841 | -1.454 | -0.008 | 0.504 | 0.711 | -0.86 | -0.938 | 0.316 | 0.383 | -1.328 | -0.599 | -0.181 | 0.167 | -0.938 | 0.293 | -0.599 |
| 02 | -1.454 | -3.126 | 1.899 | -3.126 | -1.77 | -2.584 | -0.108 | -1.77 | -2.584 | -4.4 | 1.145 | -3.126 | -2.234 | -2.234 | 1.408 | -2.234 |
| 03 | -3.126 | -4.4 | -0.658 | -4.4 | -2.234 | -4.4 | -2.234 | -4.4 | -0.181 | -2.584 | 2.629 | -3.126 | -3.126 | -3.126 | -1.328 | -4.4 |
| 04 | -3.126 | -4.4 | -0.074 | -3.126 | -4.4 | -4.4 | -2.584 | -3.126 | -1.975 | -3.126 | 2.667 | -1.77 | -4.4 | -4.4 | -3.126 | -4.4 |
| 05 | -1.975 | -4.4 | -3.126 | -4.4 | -3.126 | -4.4 | -4.4 | -4.4 | 2.384 | -2.234 | 1.416 | -1.022 | -1.6 | -4.4 | -3.126 | -4.4 |
| 06 | 2.251 | -0.721 | 0.054 | -1.6 | -2.584 | -4.4 | -3.126 | -4.4 | 1.328 | -1.6 | -1.454 | -4.4 | -3.126 | -3.126 | -4.4 | -1.215 |
| 07 | 2.528 | -3.126 | -0.22 | -4.4 | -0.346 | -4.4 | -4.4 | -4.4 | 0.244 | -3.126 | -4.4 | -4.4 | -0.721 | -4.4 | -4.4 | -4.4 |
| 08 | 0.711 | 0.785 | 1.483 | 1.851 | -4.4 | -4.4 | -2.584 | -4.4 | -4.4 | -3.126 | -4.4 | -0.26 | -4.4 | -4.4 | -4.4 | -4.4 |
| 09 | -0.439 | -0.346 | -2.234 | -0.49 | -2.234 | -0.074 | -4.4 | 0.193 | -0.346 | 0.339 | -1.114 | 0.726 | -0.49 | 0.932 | -1.215 | 1.311 |
| 10 | -1.454 | 0.383 | -1.114 | -3.126 | -0.721 | 1.611 | -2.584 | -4.4 | -3.126 | -0.658 | -1.77 | -4.4 | -0.86 | 1.946 | -1.975 | -3.126 |
| 11 | -4.4 | 0.083 | -3.126 | -3.126 | -0.26 | 2.56 | -2.234 | -1.77 | -1.215 | -2.584 | -4.4 | -1.114 | -4.4 | -3.126 | -4.4 | -3.126 |
| 12 | -2.584 | -0.392 | -1.328 | -2.584 | -0.144 | 2.548 | -1.6 | -1.215 | -3.126 | -4.4 | -2.234 | -4.4 | -3.126 | -1.77 | -2.234 | -1.328 |
| 13 | -0.938 | -1.454 | -1.022 | -3.126 | 1.511 | 1.061 | 0.316 | 1.579 | -1.454 | -1.77 | -1.6 | -2.584 | -1.022 | -4.4 | -2.234 | -1.77 |