Model info
| Transcription factor | Sox9 | ||||||||
| Model | SOX9_MOUSE.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO |  | ||||||||
| LOGO (reverse complement) | 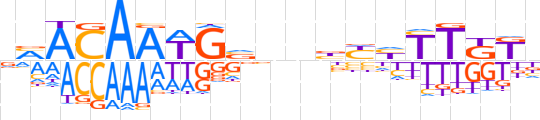 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 19 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | vMMAAdRvvnbCWTTGTKb | ||||||||
| Best auROC (human) | 0.655 | ||||||||
| Best auROC (mouse) | 0.989 | ||||||||
| Peak sets in benchmark (human) | 6 | ||||||||
| Peak sets in benchmark (mouse) | 25 | ||||||||
| Aligned words | 500 | ||||||||
| TF family | SOX-related factors {4.1.1} | ||||||||
| TF subfamily | Group E {4.1.1.5} | ||||||||
| MGI | MGI:98371 | ||||||||
| EntrezGene | GeneID:20682 (SSTAR profile) | ||||||||
| UniProt ID | SOX9_MOUSE | ||||||||
| UniProt AC | Q04887 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Sox9 expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 135.0 | 84.0 | 6.0 | 18.0 | 100.0 | 3.0 | 0.0 | 5.0 | 75.0 | 6.0 | 3.0 | 2.0 | 46.0 | 4.0 | 9.0 | 3.0 |
| 02 | 47.0 | 288.0 | 3.0 | 18.0 | 95.0 | 0.0 | 0.0 | 2.0 | 18.0 | 0.0 | 0.0 | 0.0 | 15.0 | 6.0 | 7.0 | 0.0 |
| 03 | 94.0 | 71.0 | 6.0 | 4.0 | 292.0 | 0.0 | 0.0 | 2.0 | 10.0 | 0.0 | 0.0 | 0.0 | 20.0 | 0.0 | 0.0 | 0.0 |
| 04 | 319.0 | 6.0 | 67.0 | 24.0 | 68.0 | 0.0 | 0.0 | 3.0 | 6.0 | 0.0 | 0.0 | 0.0 | 3.0 | 2.0 | 1.0 | 0.0 |
| 05 | 186.0 | 5.0 | 133.0 | 72.0 | 6.0 | 1.0 | 0.0 | 1.0 | 33.0 | 3.0 | 16.0 | 16.0 | 7.0 | 0.0 | 16.0 | 4.0 |
| 06 | 49.0 | 12.0 | 156.0 | 15.0 | 5.0 | 3.0 | 1.0 | 0.0 | 44.0 | 18.0 | 80.0 | 23.0 | 23.0 | 4.0 | 63.0 | 3.0 |
| 07 | 22.0 | 17.0 | 77.0 | 5.0 | 22.0 | 8.0 | 2.0 | 5.0 | 109.0 | 85.0 | 98.0 | 8.0 | 8.0 | 10.0 | 22.0 | 1.0 |
| 08 | 48.0 | 38.0 | 67.0 | 8.0 | 47.0 | 41.0 | 6.0 | 26.0 | 57.0 | 63.0 | 58.0 | 21.0 | 3.0 | 7.0 | 8.0 | 1.0 |
| 09 | 20.0 | 35.0 | 82.0 | 18.0 | 28.0 | 65.0 | 16.0 | 40.0 | 25.0 | 51.0 | 42.0 | 21.0 | 7.0 | 10.0 | 23.0 | 16.0 |
| 10 | 6.0 | 40.0 | 26.0 | 8.0 | 25.0 | 94.0 | 9.0 | 33.0 | 13.0 | 88.0 | 43.0 | 19.0 | 0.0 | 45.0 | 23.0 | 27.0 |
| 11 | 2.0 | 38.0 | 3.0 | 1.0 | 14.0 | 220.0 | 3.0 | 30.0 | 0.0 | 96.0 | 4.0 | 1.0 | 3.0 | 73.0 | 5.0 | 6.0 |
| 12 | 17.0 | 0.0 | 0.0 | 2.0 | 250.0 | 3.0 | 0.0 | 174.0 | 11.0 | 0.0 | 0.0 | 4.0 | 30.0 | 0.0 | 1.0 | 7.0 |
| 13 | 0.0 | 21.0 | 27.0 | 260.0 | 0.0 | 1.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 22.0 | 6.0 | 159.0 |
| 14 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 44.0 | 0.0 | 0.0 | 0.0 | 33.0 | 0.0 | 0.0 | 0.0 | 422.0 |
| 15 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 9.0 | 91.0 | 399.0 | 0.0 |
| 16 | 0.0 | 0.0 | 0.0 | 9.0 | 78.0 | 0.0 | 0.0 | 13.0 | 15.0 | 1.0 | 1.0 | 382.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 17 | 2.0 | 8.0 | 21.0 | 62.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 1.0 | 0.0 | 0.0 | 29.0 | 47.0 | 93.0 | 235.0 |
| 18 | 4.0 | 8.0 | 7.0 | 12.0 | 6.0 | 16.0 | 4.0 | 30.0 | 12.0 | 48.0 | 15.0 | 39.0 | 33.0 | 158.0 | 44.0 | 63.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 1.456 | 0.983 | -1.598 | -0.541 | 1.157 | -2.232 | -4.398 | -1.768 | 0.87 | -1.598 | -2.232 | -2.582 | 0.385 | -1.973 | -1.213 | -2.232 |
| 02 | 0.406 | 2.212 | -2.232 | -0.541 | 1.106 | -4.398 | -4.398 | -2.582 | -0.541 | -4.398 | -4.398 | -4.398 | -0.719 | -1.598 | -1.452 | -4.398 |
| 03 | 1.095 | 0.816 | -1.598 | -1.973 | 2.226 | -4.398 | -4.398 | -2.582 | -1.112 | -4.398 | -4.398 | -4.398 | -0.437 | -4.398 | -4.398 | -4.398 |
| 04 | 2.314 | -1.598 | 0.758 | -0.258 | 0.773 | -4.398 | -4.398 | -2.232 | -1.598 | -4.398 | -4.398 | -4.398 | -2.232 | -2.582 | -3.124 | -4.398 |
| 05 | 1.775 | -1.768 | 1.441 | 0.83 | -1.598 | -3.124 | -4.398 | -3.124 | 0.056 | -2.232 | -0.656 | -0.656 | -1.452 | -4.398 | -0.656 | -1.973 |
| 06 | 0.447 | -0.936 | 1.6 | -0.719 | -1.768 | -2.232 | -3.124 | -4.398 | 0.341 | -0.541 | 0.934 | -0.3 | -0.3 | -1.973 | 0.697 | -2.232 |
| 07 | -0.344 | -0.597 | 0.896 | -1.768 | -0.344 | -1.326 | -2.582 | -1.768 | 1.243 | 0.995 | 1.137 | -1.326 | -1.326 | -1.112 | -0.344 | -3.124 |
| 08 | 0.427 | 0.195 | 0.758 | -1.326 | 0.406 | 0.271 | -1.598 | -0.179 | 0.597 | 0.697 | 0.615 | -0.39 | -2.232 | -1.452 | -1.326 | -3.124 |
| 09 | -0.437 | 0.114 | 0.959 | -0.541 | -0.106 | 0.728 | -0.656 | 0.246 | -0.218 | 0.487 | 0.294 | -0.39 | -1.452 | -1.112 | -0.3 | -0.656 |
| 10 | -1.598 | 0.246 | -0.179 | -1.326 | -0.218 | 1.095 | -1.213 | 0.056 | -0.858 | 1.029 | 0.318 | -0.488 | -4.398 | 0.363 | -0.3 | -0.142 |
| 11 | -2.582 | 0.195 | -2.232 | -3.124 | -0.786 | 1.943 | -2.232 | -0.038 | -4.398 | 1.116 | -1.973 | -3.124 | -2.232 | 0.843 | -1.768 | -1.598 |
| 12 | -0.597 | -4.398 | -4.398 | -2.582 | 2.071 | -2.232 | -4.398 | 1.709 | -1.02 | -4.398 | -4.398 | -1.973 | -0.038 | -4.398 | -3.124 | -1.452 |
| 13 | -4.398 | -0.39 | -0.142 | 2.11 | -4.398 | -3.124 | -4.398 | -2.582 | -4.398 | -4.398 | -4.398 | -3.124 | -4.398 | -0.344 | -1.598 | 1.619 |
| 14 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | 0.341 | -4.398 | -4.398 | -4.398 | 0.056 | -4.398 | -4.398 | -4.398 | 2.594 |
| 15 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -4.398 | -1.213 | 1.063 | 2.538 | -4.398 |
| 16 | -4.398 | -4.398 | -4.398 | -1.213 | 0.909 | -4.398 | -4.398 | -0.858 | -0.719 | -3.124 | -3.124 | 2.494 | -4.398 | -4.398 | -4.398 | -4.398 |
| 17 | -2.582 | -1.326 | -0.39 | 0.681 | -4.398 | -4.398 | -4.398 | -3.124 | -4.398 | -3.124 | -4.398 | -4.398 | -0.072 | 0.406 | 1.084 | 2.009 |
| 18 | -1.973 | -1.326 | -1.452 | -0.936 | -1.598 | -0.656 | -1.973 | -0.038 | -0.936 | 0.427 | -0.719 | 0.221 | 0.056 | 1.613 | 0.341 | 0.697 |