Model info
| Transcription factor | Stat5b | ||||||||
| Model | STA5B_MOUSE.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 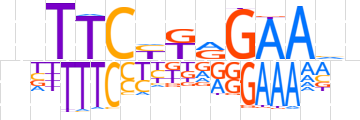 | ||||||||
| LOGO (reverse complement) |  | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 13 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | nnTTCYTRGAAvn | ||||||||
| Best auROC (human) | 0.966 | ||||||||
| Best auROC (mouse) | 0.965 | ||||||||
| Peak sets in benchmark (human) | 16 | ||||||||
| Peak sets in benchmark (mouse) | 31 | ||||||||
| Aligned words | 501 | ||||||||
| TF family | STAT factors {6.2.1} | ||||||||
| TF subfamily | STAT5B {6.2.1.0.6} | ||||||||
| MGI | MGI:103035 | ||||||||
| EntrezGene | GeneID:20851 (SSTAR profile) | ||||||||
| UniProt ID | STA5B_MOUSE | ||||||||
| UniProt AC | P42232 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Stat5b expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 35.0 | 20.0 | 56.0 | 54.0 | 13.0 | 27.0 | 6.0 | 34.0 | 25.0 | 40.0 | 27.0 | 51.0 | 11.0 | 27.0 | 15.0 | 59.0 |
| 02 | 1.0 | 1.0 | 0.0 | 82.0 | 1.0 | 0.0 | 0.0 | 113.0 | 1.0 | 0.0 | 0.0 | 103.0 | 0.0 | 3.0 | 0.0 | 195.0 |
| 03 | 0.0 | 0.0 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 | 4.0 | 0.0 | 0.0 | 0.0 | 0.0 | 18.0 | 10.0 | 6.0 | 459.0 |
| 04 | 1.0 | 17.0 | 0.0 | 0.0 | 0.0 | 10.0 | 0.0 | 0.0 | 0.0 | 6.0 | 0.0 | 0.0 | 5.0 | 452.0 | 2.0 | 7.0 |
| 05 | 0.0 | 4.0 | 1.0 | 1.0 | 41.0 | 177.0 | 13.0 | 254.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 6.0 | 0.0 | 1.0 |
| 06 | 0.0 | 0.0 | 32.0 | 9.0 | 0.0 | 0.0 | 35.0 | 154.0 | 0.0 | 0.0 | 6.0 | 8.0 | 0.0 | 0.0 | 160.0 | 96.0 |
| 07 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 132.0 | 9.0 | 78.0 | 14.0 | 78.0 | 4.0 | 173.0 | 12.0 |
| 08 | 3.0 | 1.0 | 201.0 | 5.0 | 0.0 | 0.0 | 12.0 | 1.0 | 0.0 | 0.0 | 245.0 | 6.0 | 1.0 | 0.0 | 23.0 | 2.0 |
| 09 | 3.0 | 0.0 | 1.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 443.0 | 5.0 | 11.0 | 22.0 | 9.0 | 3.0 | 1.0 | 1.0 |
| 10 | 445.0 | 3.0 | 6.0 | 2.0 | 8.0 | 0.0 | 0.0 | 0.0 | 12.0 | 1.0 | 0.0 | 0.0 | 23.0 | 0.0 | 0.0 | 0.0 |
| 11 | 219.0 | 111.0 | 82.0 | 76.0 | 2.0 | 0.0 | 1.0 | 1.0 | 4.0 | 0.0 | 2.0 | 0.0 | 0.0 | 2.0 | 0.0 | 0.0 |
| 12 | 57.0 | 48.0 | 44.0 | 76.0 | 21.0 | 29.0 | 4.0 | 59.0 | 21.0 | 25.0 | 18.0 | 21.0 | 15.0 | 16.0 | 14.0 | 32.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.112 | -0.439 | 0.578 | 0.542 | -0.86 | -0.144 | -1.6 | 0.083 | -0.22 | 0.244 | -0.144 | 0.485 | -1.022 | -0.144 | -0.721 | 0.63 |
| 02 | -3.126 | -3.126 | -4.4 | 0.957 | -3.126 | -4.4 | -4.4 | 1.276 | -3.126 | -4.4 | -4.4 | 1.184 | -4.4 | -2.234 | -4.4 | 1.821 |
| 03 | -4.4 | -4.4 | -4.4 | -2.234 | -4.4 | -4.4 | -4.4 | -1.975 | -4.4 | -4.4 | -4.4 | -4.4 | -0.543 | -1.114 | -1.6 | 2.676 |
| 04 | -3.126 | -0.599 | -4.4 | -4.4 | -4.4 | -1.114 | -4.4 | -4.4 | -4.4 | -1.6 | -4.4 | -4.4 | -1.77 | 2.66 | -2.584 | -1.454 |
| 05 | -4.4 | -1.975 | -3.126 | -3.126 | 0.269 | 1.724 | -0.86 | 2.084 | -4.4 | -2.584 | -4.4 | -4.4 | -4.4 | -1.6 | -4.4 | -3.126 |
| 06 | -4.4 | -4.4 | 0.023 | -1.215 | -4.4 | -4.4 | 0.112 | 1.585 | -4.4 | -4.4 | -1.6 | -1.328 | -4.4 | -4.4 | 1.623 | 1.114 |
| 07 | -4.4 | -4.4 | -4.4 | -4.4 | -4.4 | -4.4 | -4.4 | -4.4 | 1.431 | -1.215 | 0.907 | -0.788 | 0.907 | -1.975 | 1.701 | -0.938 |
| 08 | -2.234 | -3.126 | 1.851 | -1.77 | -4.4 | -4.4 | -0.938 | -3.126 | -4.4 | -4.4 | 2.048 | -1.6 | -3.126 | -4.4 | -0.302 | -2.584 |
| 09 | -2.234 | -4.4 | -3.126 | -4.4 | -3.126 | -4.4 | -4.4 | -4.4 | 2.64 | -1.77 | -1.022 | -0.346 | -1.215 | -2.234 | -3.126 | -3.126 |
| 10 | 2.645 | -2.234 | -1.6 | -2.584 | -1.328 | -4.4 | -4.4 | -4.4 | -0.938 | -3.126 | -4.4 | -4.4 | -0.302 | -4.4 | -4.4 | -4.4 |
| 11 | 1.936 | 1.259 | 0.957 | 0.881 | -2.584 | -4.4 | -3.126 | -3.126 | -1.975 | -4.4 | -2.584 | -4.4 | -4.4 | -2.584 | -4.4 | -4.4 |
| 12 | 0.595 | 0.425 | 0.339 | 0.881 | -0.392 | -0.074 | -1.975 | 0.63 | -0.392 | -0.22 | -0.543 | -0.392 | -0.721 | -0.658 | -0.788 | 0.023 |