Model info
| Transcription factor | Stat2 | ||||||||
| Model | STAT2_MOUSE.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO |  | ||||||||
| LOGO (reverse complement) | 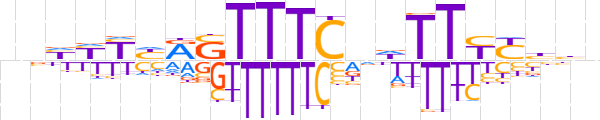 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 21 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | nvvRRAAhnGAAASYRRRdnn | ||||||||
| Best auROC (human) | 0.981 | ||||||||
| Best auROC (mouse) | 0.994 | ||||||||
| Peak sets in benchmark (human) | 11 | ||||||||
| Peak sets in benchmark (mouse) | 8 | ||||||||
| Aligned words | 509 | ||||||||
| TF family | STAT factors {6.2.1} | ||||||||
| TF subfamily | STAT2 {6.2.1.0.2} | ||||||||
| MGI | MGI:103039 | ||||||||
| EntrezGene | |||||||||
| UniProt ID | STAT2_MOUSE | ||||||||
| UniProt AC | Q9WVL2 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Stat2 expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 46.0 | 24.0 | 59.0 | 17.0 | 58.0 | 19.0 | 10.0 | 26.0 | 23.0 | 14.0 | 55.0 | 9.0 | 40.0 | 15.0 | 61.0 | 16.0 |
| 02 | 47.0 | 15.0 | 90.0 | 15.0 | 37.0 | 15.0 | 8.0 | 12.0 | 73.0 | 16.0 | 85.0 | 11.0 | 21.0 | 15.0 | 25.0 | 7.0 |
| 03 | 43.0 | 2.0 | 125.0 | 8.0 | 44.0 | 5.0 | 5.0 | 7.0 | 52.0 | 3.0 | 146.0 | 7.0 | 9.0 | 0.0 | 34.0 | 2.0 |
| 04 | 36.0 | 0.0 | 105.0 | 7.0 | 9.0 | 0.0 | 1.0 | 0.0 | 220.0 | 3.0 | 80.0 | 7.0 | 5.0 | 0.0 | 19.0 | 0.0 |
| 05 | 267.0 | 1.0 | 1.0 | 1.0 | 2.0 | 1.0 | 0.0 | 0.0 | 200.0 | 5.0 | 0.0 | 0.0 | 14.0 | 0.0 | 0.0 | 0.0 |
| 06 | 451.0 | 10.0 | 15.0 | 7.0 | 7.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 |
| 07 | 246.0 | 53.0 | 41.0 | 119.0 | 9.0 | 0.0 | 0.0 | 2.0 | 5.0 | 4.0 | 0.0 | 6.0 | 2.0 | 1.0 | 3.0 | 1.0 |
| 08 | 32.0 | 76.0 | 44.0 | 110.0 | 23.0 | 7.0 | 3.0 | 25.0 | 8.0 | 5.0 | 5.0 | 26.0 | 34.0 | 40.0 | 31.0 | 23.0 |
| 09 | 2.0 | 0.0 | 95.0 | 0.0 | 28.0 | 2.0 | 96.0 | 2.0 | 13.0 | 0.0 | 70.0 | 0.0 | 5.0 | 1.0 | 178.0 | 0.0 |
| 10 | 39.0 | 3.0 | 6.0 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 | 431.0 | 4.0 | 1.0 | 3.0 | 2.0 | 0.0 | 0.0 | 0.0 |
| 11 | 471.0 | 0.0 | 4.0 | 0.0 | 7.0 | 0.0 | 0.0 | 0.0 | 6.0 | 0.0 | 1.0 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 |
| 12 | 481.0 | 2.0 | 1.0 | 3.0 | 0.0 | 0.0 | 0.0 | 0.0 | 5.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 13 | 24.0 | 329.0 | 128.0 | 5.0 | 1.0 | 1.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 2.0 | 1.0 | 0.0 |
| 14 | 1.0 | 3.0 | 3.0 | 18.0 | 40.0 | 53.0 | 1.0 | 239.0 | 16.0 | 25.0 | 9.0 | 79.0 | 0.0 | 2.0 | 0.0 | 3.0 |
| 15 | 7.0 | 0.0 | 49.0 | 1.0 | 38.0 | 4.0 | 25.0 | 16.0 | 2.0 | 0.0 | 11.0 | 0.0 | 55.0 | 25.0 | 199.0 | 60.0 |
| 16 | 58.0 | 7.0 | 26.0 | 11.0 | 20.0 | 1.0 | 0.0 | 8.0 | 227.0 | 14.0 | 24.0 | 19.0 | 57.0 | 1.0 | 8.0 | 11.0 |
| 17 | 265.0 | 19.0 | 45.0 | 33.0 | 9.0 | 2.0 | 1.0 | 11.0 | 38.0 | 9.0 | 9.0 | 2.0 | 12.0 | 13.0 | 18.0 | 6.0 |
| 18 | 240.0 | 27.0 | 39.0 | 18.0 | 13.0 | 8.0 | 3.0 | 19.0 | 32.0 | 6.0 | 15.0 | 20.0 | 11.0 | 10.0 | 23.0 | 8.0 |
| 19 | 51.0 | 122.0 | 105.0 | 18.0 | 14.0 | 12.0 | 4.0 | 21.0 | 30.0 | 20.0 | 18.0 | 12.0 | 11.0 | 14.0 | 22.0 | 18.0 |
| 20 | 26.0 | 22.0 | 29.0 | 29.0 | 42.0 | 55.0 | 8.0 | 63.0 | 46.0 | 33.0 | 18.0 | 52.0 | 13.0 | 24.0 | 19.0 | 13.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.399 | -0.244 | 0.646 | -0.583 | 0.629 | -0.474 | -1.098 | -0.166 | -0.286 | -0.772 | 0.576 | -1.199 | 0.26 | -0.705 | 0.679 | -0.642 |
| 02 | 0.42 | -0.705 | 1.066 | -0.705 | 0.183 | -0.705 | -1.312 | -0.922 | 0.857 | -0.642 | 1.009 | -1.006 | -0.376 | -0.705 | -0.204 | -1.439 |
| 03 | 0.332 | -2.568 | 1.393 | -1.312 | 0.355 | -1.754 | -1.754 | -1.439 | 0.52 | -2.218 | 1.548 | -1.439 | -1.199 | -4.387 | 0.099 | -2.568 |
| 04 | 0.156 | -4.387 | 1.219 | -1.439 | -1.199 | -4.387 | -3.111 | -4.387 | 1.957 | -2.218 | 0.948 | -1.439 | -1.754 | -4.387 | -0.474 | -4.387 |
| 05 | 2.15 | -3.111 | -3.111 | -3.111 | -2.568 | -3.111 | -4.387 | -4.387 | 1.862 | -1.754 | -4.387 | -4.387 | -0.772 | -4.387 | -4.387 | -4.387 |
| 06 | 2.674 | -1.098 | -0.705 | -1.439 | -1.439 | -4.387 | -4.387 | -4.387 | -4.387 | -3.111 | -4.387 | -4.387 | -3.111 | -4.387 | -4.387 | -4.387 |
| 07 | 2.068 | 0.539 | 0.285 | 1.344 | -1.199 | -4.387 | -4.387 | -2.568 | -1.754 | -1.96 | -4.387 | -1.584 | -2.568 | -3.111 | -2.218 | -3.111 |
| 08 | 0.039 | 0.897 | 0.355 | 1.266 | -0.286 | -1.439 | -2.218 | -0.204 | -1.312 | -1.754 | -1.754 | -0.166 | 0.099 | 0.26 | 0.008 | -0.286 |
| 09 | -2.568 | -4.387 | 1.12 | -4.387 | -0.092 | -2.568 | 1.13 | -2.568 | -0.844 | -4.387 | 0.816 | -4.387 | -1.754 | -3.111 | 1.746 | -4.387 |
| 10 | 0.235 | -2.218 | -1.584 | -4.387 | -2.218 | -4.387 | -4.387 | -4.387 | 2.629 | -1.96 | -3.111 | -2.218 | -2.568 | -4.387 | -4.387 | -4.387 |
| 11 | 2.717 | -4.387 | -1.96 | -4.387 | -1.439 | -4.387 | -4.387 | -4.387 | -1.584 | -4.387 | -3.111 | -4.387 | -2.218 | -4.387 | -4.387 | -4.387 |
| 12 | 2.738 | -2.568 | -3.111 | -2.218 | -4.387 | -4.387 | -4.387 | -4.387 | -1.754 | -4.387 | -4.387 | -4.387 | -4.387 | -4.387 | -4.387 | -4.387 |
| 13 | -0.244 | 2.359 | 1.417 | -1.754 | -3.111 | -3.111 | -4.387 | -4.387 | -4.387 | -3.111 | -4.387 | -4.387 | -4.387 | -2.568 | -3.111 | -4.387 |
| 14 | -3.111 | -2.218 | -2.218 | -0.527 | 0.26 | 0.539 | -3.111 | 2.04 | -0.642 | -0.204 | -1.199 | 0.936 | -4.387 | -2.568 | -4.387 | -2.218 |
| 15 | -1.439 | -4.387 | 0.461 | -3.111 | 0.209 | -1.96 | -0.204 | -0.642 | -2.568 | -4.387 | -1.006 | -4.387 | 0.576 | -0.204 | 1.857 | 0.662 |
| 16 | 0.629 | -1.439 | -0.166 | -1.006 | -0.423 | -3.111 | -4.387 | -1.312 | 1.988 | -0.772 | -0.244 | -0.474 | 0.611 | -3.111 | -1.312 | -1.006 |
| 17 | 2.143 | -0.474 | 0.377 | 0.07 | -1.199 | -2.568 | -3.111 | -1.006 | 0.209 | -1.199 | -1.199 | -2.568 | -0.922 | -0.844 | -0.527 | -1.584 |
| 18 | 2.044 | -0.128 | 0.235 | -0.527 | -0.844 | -1.312 | -2.218 | -0.474 | 0.039 | -1.584 | -0.705 | -0.423 | -1.006 | -1.098 | -0.286 | -1.312 |
| 19 | 0.501 | 1.369 | 1.219 | -0.527 | -0.772 | -0.922 | -1.96 | -0.376 | -0.024 | -0.423 | -0.527 | -0.922 | -1.006 | -0.772 | -0.33 | -0.527 |
| 20 | -0.166 | -0.33 | -0.058 | -0.058 | 0.308 | 0.576 | -1.312 | 0.711 | 0.399 | 0.07 | -0.527 | 0.52 | -0.844 | -0.244 | -0.474 | -0.844 |