Model info
| Transcription factor | ZBTB6 (GeneCards) | ||||||||
| Model | ZBTB6_HUMAN.H11DI.0.C | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 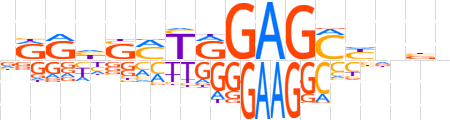 | ||||||||
| LOGO (reverse complement) |  | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 16 | ||||||||
| Quality | C | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | vRRhSMTRGAGChdbn | ||||||||
| Best auROC (human) | 0.89 | ||||||||
| Best auROC (mouse) | |||||||||
| Peak sets in benchmark (human) | 2 | ||||||||
| Peak sets in benchmark (mouse) | |||||||||
| Aligned words | 543 | ||||||||
| TF family | More than 3 adjacent zinc finger factors {2.3.3} | ||||||||
| TF subfamily | ZBTB6-like factors {2.3.3.11} | ||||||||
| HGNC | HGNC:16764 | ||||||||
| EntrezGene | GeneID:10773 (SSTAR profile) | ||||||||
| UniProt ID | ZBTB6_HUMAN | ||||||||
| UniProt AC | Q15916 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | ZBTB6 expression | ||||||||
| ReMap ChIP-seq dataset list | ZBTB6 datasets | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 17.0 | 2.0 | 89.0 | 6.0 | 15.0 | 10.0 | 58.0 | 25.0 | 22.0 | 6.0 | 155.0 | 13.0 | 8.0 | 8.0 | 51.0 | 11.0 |
| 02 | 13.0 | 1.0 | 47.0 | 1.0 | 17.0 | 2.0 | 7.0 | 0.0 | 83.0 | 11.0 | 251.0 | 8.0 | 13.0 | 2.0 | 39.0 | 1.0 |
| 03 | 13.0 | 12.0 | 9.0 | 92.0 | 5.0 | 1.0 | 6.0 | 4.0 | 91.0 | 138.0 | 3.0 | 112.0 | 1.0 | 3.0 | 0.0 | 6.0 |
| 04 | 7.0 | 15.0 | 82.0 | 6.0 | 2.0 | 9.0 | 120.0 | 23.0 | 0.0 | 11.0 | 5.0 | 2.0 | 7.0 | 43.0 | 140.0 | 24.0 |
| 05 | 6.0 | 9.0 | 1.0 | 0.0 | 28.0 | 49.0 | 0.0 | 1.0 | 137.0 | 179.0 | 26.0 | 5.0 | 8.0 | 43.0 | 4.0 | 0.0 |
| 06 | 9.0 | 18.0 | 6.0 | 146.0 | 16.0 | 41.0 | 2.0 | 221.0 | 0.0 | 7.0 | 0.0 | 24.0 | 1.0 | 1.0 | 0.0 | 4.0 |
| 07 | 7.0 | 0.0 | 16.0 | 3.0 | 20.0 | 1.0 | 34.0 | 12.0 | 0.0 | 0.0 | 7.0 | 1.0 | 67.0 | 3.0 | 296.0 | 29.0 |
| 08 | 0.0 | 0.0 | 94.0 | 0.0 | 0.0 | 0.0 | 4.0 | 0.0 | 4.0 | 1.0 | 347.0 | 1.0 | 0.0 | 0.0 | 45.0 | 0.0 |
| 09 | 0.0 | 0.0 | 0.0 | 4.0 | 1.0 | 0.0 | 0.0 | 0.0 | 488.0 | 0.0 | 0.0 | 2.0 | 1.0 | 0.0 | 0.0 | 0.0 |
| 10 | 2.0 | 3.0 | 484.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 5.0 |
| 11 | 1.0 | 1.0 | 0.0 | 0.0 | 1.0 | 2.0 | 0.0 | 0.0 | 94.0 | 372.0 | 16.0 | 3.0 | 0.0 | 6.0 | 0.0 | 0.0 |
| 12 | 22.0 | 48.0 | 13.0 | 13.0 | 25.0 | 228.0 | 33.0 | 95.0 | 4.0 | 8.0 | 0.0 | 4.0 | 0.0 | 2.0 | 1.0 | 0.0 |
| 13 | 18.0 | 4.0 | 24.0 | 5.0 | 106.0 | 42.0 | 73.0 | 65.0 | 11.0 | 18.0 | 15.0 | 3.0 | 12.0 | 19.0 | 70.0 | 11.0 |
| 14 | 18.0 | 29.0 | 86.0 | 14.0 | 13.0 | 20.0 | 27.0 | 23.0 | 21.0 | 56.0 | 87.0 | 18.0 | 3.0 | 23.0 | 39.0 | 19.0 |
| 15 | 14.0 | 2.0 | 30.0 | 9.0 | 29.0 | 32.0 | 29.0 | 38.0 | 91.0 | 47.0 | 72.0 | 29.0 | 18.0 | 17.0 | 20.0 | 19.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | -0.591 | -2.576 | 1.047 | -1.592 | -0.713 | -1.106 | 0.621 | -0.212 | -0.338 | -1.592 | 1.6 | -0.852 | -1.32 | -1.32 | 0.493 | -1.014 |
| 02 | -0.852 | -3.119 | 0.412 | -3.119 | -0.591 | -2.576 | -1.447 | -4.393 | 0.977 | -1.014 | 2.081 | -1.32 | -0.852 | -2.576 | 0.227 | -3.119 |
| 03 | -0.852 | -0.93 | -1.207 | 1.08 | -1.762 | -3.119 | -1.592 | -1.968 | 1.069 | 1.484 | -2.226 | 1.276 | -3.119 | -2.226 | -4.393 | -1.592 |
| 04 | -1.447 | -0.713 | 0.965 | -1.592 | -2.576 | -1.207 | 1.344 | -0.294 | -4.393 | -1.014 | -1.762 | -2.576 | -1.447 | 0.324 | 1.498 | -0.252 |
| 05 | -1.592 | -1.207 | -3.119 | -4.393 | -0.1 | 0.453 | -4.393 | -3.119 | 1.476 | 1.743 | -0.174 | -1.762 | -1.32 | 0.324 | -1.968 | -4.393 |
| 06 | -1.207 | -0.535 | -1.592 | 1.54 | -0.65 | 0.277 | -2.576 | 1.953 | -4.393 | -1.447 | -4.393 | -0.252 | -3.119 | -3.119 | -4.393 | -1.968 |
| 07 | -1.447 | -4.393 | -0.65 | -2.226 | -0.431 | -3.119 | 0.091 | -0.93 | -4.393 | -4.393 | -1.447 | -3.119 | 0.764 | -2.226 | 2.245 | -0.066 |
| 08 | -4.393 | -4.393 | 1.101 | -4.393 | -4.393 | -4.393 | -1.968 | -4.393 | -1.968 | -3.119 | 2.404 | -3.119 | -4.393 | -4.393 | 0.369 | -4.393 |
| 09 | -4.393 | -4.393 | -4.393 | -1.968 | -3.119 | -4.393 | -4.393 | -4.393 | 2.745 | -4.393 | -4.393 | -2.576 | -3.119 | -4.393 | -4.393 | -4.393 |
| 10 | -2.576 | -2.226 | 2.736 | -3.119 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -4.393 | -3.119 | -1.762 |
| 11 | -3.119 | -3.119 | -4.393 | -4.393 | -3.119 | -2.576 | -4.393 | -4.393 | 1.101 | 2.474 | -0.65 | -2.226 | -4.393 | -1.592 | -4.393 | -4.393 |
| 12 | -0.338 | 0.433 | -0.852 | -0.852 | -0.212 | 1.985 | 0.062 | 1.112 | -1.968 | -1.32 | -4.393 | -1.968 | -4.393 | -2.576 | -3.119 | -4.393 |
| 13 | -0.535 | -1.968 | -0.252 | -1.762 | 1.221 | 0.3 | 0.849 | 0.734 | -1.014 | -0.535 | -0.713 | -2.226 | -0.93 | -0.482 | 0.808 | -1.014 |
| 14 | -0.535 | -0.066 | 1.012 | -0.78 | -0.852 | -0.431 | -0.136 | -0.294 | -0.384 | 0.586 | 1.024 | -0.535 | -2.226 | -0.294 | 0.227 | -0.482 |
| 15 | -0.78 | -2.576 | -0.032 | -1.207 | -0.066 | 0.031 | -0.066 | 0.201 | 1.069 | 0.412 | 0.836 | -0.066 | -0.535 | -0.591 | -0.431 | -0.482 |