Model info
| Transcription factor | ZNF143 (GeneCards) | ||||||||
| Model | ZN143_HUMAN.H11DI.0.A | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 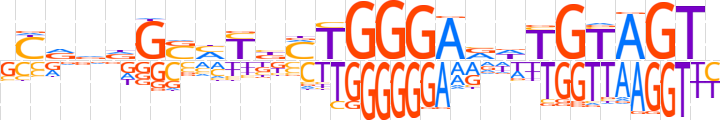 | ||||||||
| LOGO (reverse complement) | 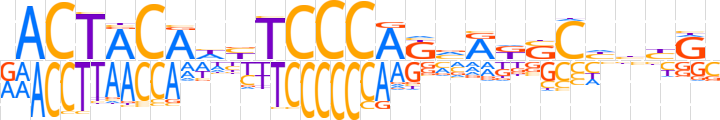 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 25 | ||||||||
| Quality | A | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | SYvvdGSMYbMTGGGARdTGTAGTY | ||||||||
| Best auROC (human) | 0.993 | ||||||||
| Best auROC (mouse) | 0.987 | ||||||||
| Peak sets in benchmark (human) | 28 | ||||||||
| Peak sets in benchmark (mouse) | 9 | ||||||||
| Aligned words | 386 | ||||||||
| TF family | More than 3 adjacent zinc finger factors {2.3.3} | ||||||||
| TF subfamily | ZNF76-like factors {2.3.3.28} | ||||||||
| HGNC | HGNC:12928 | ||||||||
| EntrezGene | GeneID:7702 (SSTAR profile) | ||||||||
| UniProt ID | ZN143_HUMAN | ||||||||
| UniProt AC | P52747 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | ZNF143 expression | ||||||||
| ReMap ChIP-seq dataset list | ZNF143 datasets | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.0 | 13.0 | 3.0 | 0.0 | 13.0 | 63.0 | 10.0 | 18.0 | 13.0 | 211.0 | 5.0 | 12.0 | 0.0 | 12.0 | 5.0 | 2.0 |
| 02 | 9.0 | 3.0 | 12.0 | 2.0 | 109.0 | 14.0 | 150.0 | 26.0 | 5.0 | 10.0 | 8.0 | 0.0 | 10.0 | 5.0 | 17.0 | 0.0 |
| 03 | 45.0 | 19.0 | 53.0 | 16.0 | 10.0 | 1.0 | 15.0 | 6.0 | 40.0 | 42.0 | 80.0 | 25.0 | 8.0 | 7.0 | 8.0 | 5.0 |
| 04 | 20.0 | 7.0 | 65.0 | 11.0 | 15.0 | 1.0 | 32.0 | 21.0 | 48.0 | 6.0 | 68.0 | 34.0 | 10.0 | 0.0 | 18.0 | 24.0 |
| 05 | 3.0 | 0.0 | 89.0 | 1.0 | 0.0 | 1.0 | 12.0 | 1.0 | 7.0 | 4.0 | 158.0 | 14.0 | 1.0 | 0.0 | 84.0 | 5.0 |
| 06 | 1.0 | 7.0 | 3.0 | 0.0 | 0.0 | 2.0 | 3.0 | 0.0 | 21.0 | 226.0 | 80.0 | 16.0 | 0.0 | 12.0 | 6.0 | 3.0 |
| 07 | 13.0 | 5.0 | 1.0 | 3.0 | 123.0 | 95.0 | 11.0 | 18.0 | 38.0 | 44.0 | 2.0 | 8.0 | 7.0 | 8.0 | 3.0 | 1.0 |
| 08 | 1.0 | 35.0 | 17.0 | 128.0 | 0.0 | 32.0 | 3.0 | 117.0 | 0.0 | 6.0 | 1.0 | 10.0 | 1.0 | 5.0 | 2.0 | 22.0 |
| 09 | 0.0 | 2.0 | 0.0 | 0.0 | 6.0 | 11.0 | 28.0 | 33.0 | 1.0 | 2.0 | 18.0 | 2.0 | 8.0 | 60.0 | 104.0 | 105.0 |
| 10 | 2.0 | 12.0 | 0.0 | 1.0 | 21.0 | 43.0 | 3.0 | 8.0 | 11.0 | 124.0 | 5.0 | 10.0 | 6.0 | 100.0 | 27.0 | 7.0 |
| 11 | 1.0 | 16.0 | 0.0 | 23.0 | 2.0 | 29.0 | 2.0 | 246.0 | 0.0 | 6.0 | 0.0 | 29.0 | 0.0 | 12.0 | 0.0 | 14.0 |
| 12 | 0.0 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 | 63.0 | 0.0 | 0.0 | 0.0 | 2.0 | 0.0 | 2.0 | 0.0 | 309.0 | 1.0 |
| 13 | 0.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 376.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 |
| 14 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 2.0 | 1.0 | 371.0 | 5.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 15 | 2.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 342.0 | 5.0 | 18.0 | 7.0 | 3.0 | 2.0 | 0.0 | 0.0 |
| 16 | 166.0 | 26.0 | 135.0 | 21.0 | 4.0 | 2.0 | 1.0 | 0.0 | 6.0 | 2.0 | 10.0 | 0.0 | 5.0 | 0.0 | 2.0 | 0.0 |
| 17 | 104.0 | 9.0 | 29.0 | 39.0 | 3.0 | 2.0 | 1.0 | 24.0 | 29.0 | 12.0 | 10.0 | 97.0 | 2.0 | 1.0 | 1.0 | 17.0 |
| 18 | 1.0 | 8.0 | 6.0 | 123.0 | 1.0 | 2.0 | 2.0 | 19.0 | 1.0 | 9.0 | 1.0 | 30.0 | 3.0 | 14.0 | 15.0 | 145.0 |
| 19 | 0.0 | 0.0 | 6.0 | 0.0 | 1.0 | 0.0 | 32.0 | 0.0 | 0.0 | 0.0 | 24.0 | 0.0 | 5.0 | 0.0 | 311.0 | 1.0 |
| 20 | 0.0 | 1.0 | 4.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 16.0 | 20.0 | 14.0 | 323.0 | 0.0 | 0.0 | 0.0 | 1.0 |
| 21 | 13.0 | 0.0 | 2.0 | 1.0 | 16.0 | 2.0 | 2.0 | 1.0 | 16.0 | 1.0 | 1.0 | 0.0 | 310.0 | 0.0 | 14.0 | 1.0 |
| 22 | 1.0 | 1.0 | 353.0 | 0.0 | 1.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 19.0 | 0.0 | 0.0 | 1.0 | 2.0 | 0.0 |
| 23 | 0.0 | 0.0 | 1.0 | 1.0 | 1.0 | 0.0 | 1.0 | 0.0 | 0.0 | 2.0 | 4.0 | 370.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 24 | 1.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 1.0 | 3.0 | 1.0 | 1.0 | 10.0 | 186.0 | 9.0 | 166.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | -4.174 | -0.59 | -1.968 | -4.174 | -0.59 | 0.966 | -0.844 | -0.272 | -0.59 | 2.171 | -1.502 | -0.668 | -4.174 | -0.668 | -1.502 | -2.32 |
| 02 | -0.945 | -1.968 | -0.668 | -2.32 | 1.512 | -0.518 | 1.83 | 0.089 | -1.502 | -0.844 | -1.058 | -4.174 | -0.844 | -1.502 | -0.328 | -4.174 |
| 03 | 0.632 | -0.219 | 0.794 | -0.388 | -0.844 | -2.867 | -0.451 | -1.331 | 0.515 | 0.563 | 1.204 | 0.051 | -1.058 | -1.186 | -1.058 | -1.502 |
| 04 | -0.169 | -1.186 | 0.997 | -0.752 | -0.451 | -2.867 | 0.294 | -0.121 | 0.696 | -1.331 | 1.042 | 0.354 | -0.844 | -4.174 | -0.272 | 0.01 |
| 05 | -1.968 | -4.174 | 1.31 | -2.867 | -4.174 | -2.867 | -0.668 | -2.867 | -1.186 | -1.708 | 1.882 | -0.518 | -2.867 | -4.174 | 1.252 | -1.502 |
| 06 | -2.867 | -1.186 | -1.968 | -4.174 | -4.174 | -2.32 | -1.968 | -4.174 | -0.121 | 2.239 | 1.204 | -0.388 | -4.174 | -0.668 | -1.331 | -1.968 |
| 07 | -0.59 | -1.502 | -2.867 | -1.968 | 1.632 | 1.375 | -0.752 | -0.272 | 0.464 | 0.609 | -2.32 | -1.058 | -1.186 | -1.058 | -1.968 | -2.867 |
| 08 | -2.867 | 0.383 | -0.328 | 1.672 | -4.174 | 0.294 | -1.968 | 1.582 | -4.174 | -1.331 | -2.867 | -0.844 | -2.867 | -1.502 | -2.32 | -0.075 |
| 09 | -4.174 | -2.32 | -4.174 | -4.174 | -1.331 | -0.752 | 0.162 | 0.325 | -2.867 | -2.32 | -0.272 | -2.32 | -1.058 | 0.917 | 1.465 | 1.474 |
| 10 | -2.32 | -0.668 | -4.174 | -2.867 | -0.121 | 0.587 | -1.968 | -1.058 | -0.752 | 1.64 | -1.502 | -0.844 | -1.331 | 1.426 | 0.126 | -1.186 |
| 11 | -2.867 | -0.388 | -4.174 | -0.032 | -2.32 | 0.197 | -2.32 | 2.324 | -4.174 | -1.331 | -4.174 | 0.197 | -4.174 | -0.668 | -4.174 | -0.518 |
| 12 | -4.174 | -4.174 | -1.968 | -4.174 | -4.174 | -4.174 | 0.966 | -4.174 | -4.174 | -4.174 | -2.32 | -4.174 | -2.32 | -4.174 | 2.551 | -2.867 |
| 13 | -4.174 | -4.174 | -2.32 | -4.174 | -4.174 | -4.174 | -4.174 | -4.174 | -2.867 | -4.174 | 2.747 | -4.174 | -4.174 | -4.174 | -2.867 | -4.174 |
| 14 | -4.174 | -4.174 | -2.867 | -4.174 | -4.174 | -4.174 | -4.174 | -4.174 | -2.32 | -2.867 | 2.734 | -1.502 | -4.174 | -4.174 | -4.174 | -4.174 |
| 15 | -2.32 | -4.174 | -4.174 | -4.174 | -2.867 | -4.174 | -4.174 | -4.174 | 2.653 | -1.502 | -0.272 | -1.186 | -1.968 | -2.32 | -4.174 | -4.174 |
| 16 | 1.931 | 0.089 | 1.725 | -0.121 | -1.708 | -2.32 | -2.867 | -4.174 | -1.331 | -2.32 | -0.844 | -4.174 | -1.502 | -4.174 | -2.32 | -4.174 |
| 17 | 1.465 | -0.945 | 0.197 | 0.49 | -1.968 | -2.32 | -2.867 | 0.01 | 0.197 | -0.668 | -0.844 | 1.395 | -2.32 | -2.867 | -2.867 | -0.328 |
| 18 | -2.867 | -1.058 | -1.331 | 1.632 | -2.867 | -2.32 | -2.32 | -0.219 | -2.867 | -0.945 | -2.867 | 0.23 | -1.968 | -0.518 | -0.451 | 1.796 |
| 19 | -4.174 | -4.174 | -1.331 | -4.174 | -2.867 | -4.174 | 0.294 | -4.174 | -4.174 | -4.174 | 0.01 | -4.174 | -1.502 | -4.174 | 2.558 | -2.867 |
| 20 | -4.174 | -2.867 | -1.708 | -2.867 | -4.174 | -4.174 | -4.174 | -4.174 | -0.388 | -0.169 | -0.518 | 2.596 | -4.174 | -4.174 | -4.174 | -2.867 |
| 21 | -0.59 | -4.174 | -2.32 | -2.867 | -0.388 | -2.32 | -2.32 | -2.867 | -0.388 | -2.867 | -2.867 | -4.174 | 2.555 | -4.174 | -0.518 | -2.867 |
| 22 | -2.867 | -2.867 | 2.684 | -4.174 | -2.867 | -4.174 | -2.32 | -4.174 | -4.174 | -4.174 | -0.219 | -4.174 | -4.174 | -2.867 | -2.32 | -4.174 |
| 23 | -4.174 | -4.174 | -2.867 | -2.867 | -2.867 | -4.174 | -2.867 | -4.174 | -4.174 | -2.32 | -1.708 | 2.731 | -4.174 | -4.174 | -4.174 | -4.174 |
| 24 | -2.867 | -4.174 | -4.174 | -4.174 | -2.867 | -4.174 | -4.174 | -2.867 | -2.867 | -1.968 | -2.867 | -2.867 | -0.844 | 2.045 | -0.945 | 1.931 |