Model info
| Transcription factor | ZNF528 (GeneCards) | ||||||||
| Model | ZN528_HUMAN.H11DI.0.C | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO |  | ||||||||
| LOGO (reverse complement) | 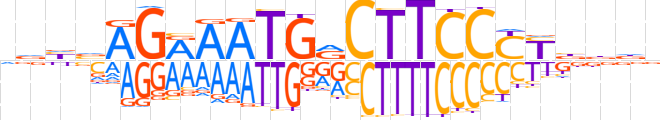 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 23 | ||||||||
| Quality | C | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | nhhvRGGGAAGYCATTYCTbdbb | ||||||||
| Best auROC (human) | 0.805 | ||||||||
| Best auROC (mouse) | |||||||||
| Peak sets in benchmark (human) | 2 | ||||||||
| Peak sets in benchmark (mouse) | |||||||||
| Aligned words | 312 | ||||||||
| TF family | More than 3 adjacent zinc finger factors {2.3.3} | ||||||||
| TF subfamily | unclassified {2.3.3.0} | ||||||||
| HGNC | HGNC:29384 | ||||||||
| EntrezGene | GeneID:84436 (SSTAR profile) | ||||||||
| UniProt ID | ZN528_HUMAN | ||||||||
| UniProt AC | Q3MIS6 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | ZNF528 expression | ||||||||
| ReMap ChIP-seq dataset list | ZNF528 datasets | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 26.0 | 29.0 | 12.0 | 14.0 | 18.0 | 70.0 | 0.0 | 15.0 | 14.0 | 46.0 | 17.0 | 12.0 | 5.0 | 12.0 | 15.0 | 6.0 |
| 02 | 22.0 | 14.0 | 16.0 | 11.0 | 19.0 | 107.0 | 2.0 | 29.0 | 16.0 | 7.0 | 13.0 | 8.0 | 12.0 | 13.0 | 12.0 | 10.0 |
| 03 | 31.0 | 13.0 | 18.0 | 7.0 | 18.0 | 112.0 | 2.0 | 9.0 | 17.0 | 7.0 | 12.0 | 7.0 | 13.0 | 19.0 | 14.0 | 12.0 |
| 04 | 53.0 | 3.0 | 17.0 | 6.0 | 144.0 | 3.0 | 2.0 | 2.0 | 25.0 | 6.0 | 14.0 | 1.0 | 5.0 | 2.0 | 21.0 | 7.0 |
| 05 | 22.0 | 1.0 | 198.0 | 6.0 | 6.0 | 1.0 | 2.0 | 5.0 | 18.0 | 0.0 | 31.0 | 5.0 | 7.0 | 0.0 | 8.0 | 1.0 |
| 06 | 0.0 | 0.0 | 53.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 5.0 | 0.0 | 234.0 | 0.0 | 5.0 | 0.0 | 11.0 | 1.0 |
| 07 | 0.0 | 0.0 | 12.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 16.0 | 1.0 | 280.0 | 1.0 | 0.0 | 0.0 | 1.0 | 0.0 |
| 08 | 16.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 293.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 |
| 09 | 295.0 | 1.0 | 13.0 | 1.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 10 | 0.0 | 0.0 | 296.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 13.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 |
| 11 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 16.0 | 159.0 | 20.0 | 116.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 12 | 1.0 | 14.0 | 0.0 | 1.0 | 12.0 | 146.0 | 0.0 | 1.0 | 1.0 | 18.0 | 0.0 | 1.0 | 13.0 | 103.0 | 0.0 | 0.0 |
| 13 | 12.0 | 2.0 | 12.0 | 1.0 | 280.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 |
| 14 | 1.0 | 22.0 | 2.0 | 270.0 | 0.0 | 0.0 | 0.0 | 3.0 | 1.0 | 9.0 | 1.0 | 1.0 | 0.0 | 0.0 | 0.0 | 1.0 |
| 15 | 0.0 | 0.0 | 0.0 | 2.0 | 1.0 | 2.0 | 0.0 | 28.0 | 0.0 | 1.0 | 0.0 | 2.0 | 0.0 | 34.0 | 4.0 | 237.0 |
| 16 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 23.0 | 5.0 | 8.0 | 0.0 | 1.0 | 3.0 | 0.0 | 1.0 | 23.0 | 26.0 | 219.0 |
| 17 | 0.0 | 1.0 | 0.0 | 1.0 | 0.0 | 46.0 | 0.0 | 2.0 | 1.0 | 31.0 | 0.0 | 2.0 | 0.0 | 222.0 | 0.0 | 5.0 |
| 18 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 51.0 | 1.0 | 247.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 2.0 | 0.0 | 8.0 |
| 19 | 1.0 | 0.0 | 0.0 | 0.0 | 8.0 | 26.0 | 6.0 | 14.0 | 0.0 | 0.0 | 1.0 | 0.0 | 17.0 | 58.0 | 139.0 | 41.0 |
| 20 | 13.0 | 3.0 | 7.0 | 3.0 | 38.0 | 16.0 | 4.0 | 26.0 | 103.0 | 11.0 | 26.0 | 6.0 | 19.0 | 10.0 | 13.0 | 13.0 |
| 21 | 15.0 | 99.0 | 26.0 | 33.0 | 14.0 | 12.0 | 4.0 | 10.0 | 13.0 | 18.0 | 13.0 | 6.0 | 6.0 | 19.0 | 12.0 | 11.0 |
| 22 | 9.0 | 12.0 | 17.0 | 10.0 | 19.0 | 32.0 | 2.0 | 95.0 | 17.0 | 14.0 | 17.0 | 7.0 | 6.0 | 16.0 | 16.0 | 22.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.286 | 0.394 | -0.471 | -0.321 | -0.075 | 1.268 | -4.011 | -0.254 | -0.321 | 0.851 | -0.131 | -0.471 | -1.307 | -0.471 | -0.254 | -1.136 |
| 02 | 0.122 | -0.321 | -0.191 | -0.556 | -0.022 | 1.691 | -2.127 | 0.394 | -0.191 | -0.99 | -0.393 | -0.862 | -0.471 | -0.393 | -0.471 | -0.648 |
| 03 | 0.46 | -0.393 | -0.075 | -0.99 | -0.075 | 1.736 | -2.127 | -0.749 | -0.131 | -0.99 | -0.471 | -0.99 | -0.393 | -0.022 | -0.321 | -0.471 |
| 04 | 0.992 | -1.774 | -0.131 | -1.136 | 1.987 | -1.774 | -2.127 | -2.127 | 0.248 | -1.136 | -0.321 | -2.679 | -1.307 | -2.127 | 0.076 | -0.99 |
| 05 | 0.122 | -2.679 | 2.305 | -1.136 | -1.136 | -2.679 | -2.127 | -1.307 | -0.075 | -4.011 | 0.46 | -1.307 | -0.99 | -4.011 | -0.862 | -2.679 |
| 06 | -4.011 | -4.011 | 0.992 | -4.011 | -2.127 | -4.011 | -4.011 | -4.011 | -1.307 | -4.011 | 2.471 | -4.011 | -1.307 | -4.011 | -0.556 | -2.679 |
| 07 | -4.011 | -4.011 | -0.471 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -0.191 | -2.679 | 2.651 | -2.679 | -4.011 | -4.011 | -2.679 | -4.011 |
| 08 | -0.191 | -4.011 | -4.011 | -4.011 | -2.679 | -4.011 | -4.011 | -4.011 | 2.696 | -4.011 | -4.011 | -4.011 | -4.011 | -2.679 | -4.011 | -4.011 |
| 09 | 2.703 | -2.679 | -0.393 | -2.679 | -2.679 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 |
| 10 | -4.011 | -4.011 | 2.706 | -4.011 | -4.011 | -4.011 | -2.679 | -4.011 | -4.011 | -4.011 | -0.393 | -4.011 | -4.011 | -4.011 | -2.679 | -4.011 |
| 11 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -0.191 | 2.086 | 0.028 | 1.771 | -4.011 | -4.011 | -4.011 | -4.011 |
| 12 | -2.679 | -0.321 | -4.011 | -2.679 | -0.471 | 2.001 | -4.011 | -2.679 | -2.679 | -0.075 | -4.011 | -2.679 | -0.393 | 1.653 | -4.011 | -4.011 |
| 13 | -0.471 | -2.127 | -0.471 | -2.679 | 2.651 | -2.679 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -1.774 | -4.011 | -4.011 | -4.011 |
| 14 | -2.679 | 0.122 | -2.127 | 2.614 | -4.011 | -4.011 | -4.011 | -1.774 | -2.679 | -0.749 | -2.679 | -2.679 | -4.011 | -4.011 | -4.011 | -2.679 |
| 15 | -4.011 | -4.011 | -4.011 | -2.127 | -2.679 | -2.127 | -4.011 | 0.359 | -4.011 | -2.679 | -4.011 | -2.127 | -4.011 | 0.551 | -1.513 | 2.484 |
| 16 | -4.011 | -2.679 | -4.011 | -4.011 | -2.679 | 0.165 | -1.307 | -0.862 | -4.011 | -2.679 | -1.774 | -4.011 | -2.679 | 0.165 | 0.286 | 2.405 |
| 17 | -4.011 | -2.679 | -4.011 | -2.679 | -4.011 | 0.851 | -4.011 | -2.127 | -2.679 | 0.46 | -4.011 | -2.127 | -4.011 | 2.419 | -4.011 | -1.307 |
| 18 | -4.011 | -2.679 | -4.011 | -4.011 | -2.679 | 0.953 | -2.679 | 2.525 | -4.011 | -4.011 | -4.011 | -4.011 | -4.011 | -2.127 | -4.011 | -0.862 |
| 19 | -2.679 | -4.011 | -4.011 | -4.011 | -0.862 | 0.286 | -1.136 | -0.321 | -4.011 | -4.011 | -2.679 | -4.011 | -0.131 | 1.081 | 1.952 | 0.737 |
| 20 | -0.393 | -1.774 | -0.99 | -1.774 | 0.661 | -0.191 | -1.513 | 0.286 | 1.653 | -0.556 | 0.286 | -1.136 | -0.022 | -0.648 | -0.393 | -0.393 |
| 21 | -0.254 | 1.613 | 0.286 | 0.522 | -0.321 | -0.471 | -1.513 | -0.648 | -0.393 | -0.075 | -0.393 | -1.136 | -1.136 | -0.022 | -0.471 | -0.556 |
| 22 | -0.749 | -0.471 | -0.131 | -0.648 | -0.022 | 0.491 | -2.127 | 1.572 | -0.131 | -0.321 | -0.131 | -0.99 | -1.136 | -0.191 | -0.191 | 0.122 |