Model info
| Transcription factor | ZSCAN31 (GeneCards) | ||||||||
| Model | ZSC31_HUMAN.H11DI.0.C | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 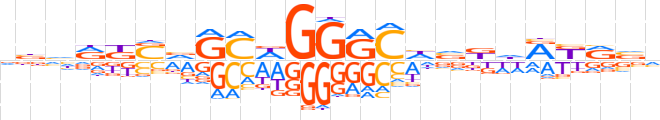 | ||||||||
| LOGO (reverse complement) | 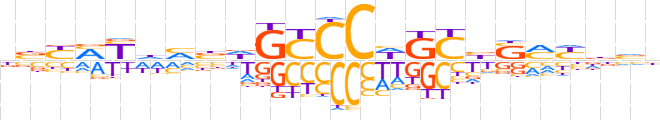 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 23 | ||||||||
| Quality | C | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | vbhRKSvGMWGGGChvKdRKRvh | ||||||||
| Best auROC (human) | 0.914 | ||||||||
| Best auROC (mouse) | |||||||||
| Peak sets in benchmark (human) | 4 | ||||||||
| Peak sets in benchmark (mouse) | |||||||||
| Aligned words | 270 | ||||||||
| TF family | More than 3 adjacent zinc finger factors {2.3.3} | ||||||||
| TF subfamily | ZNF24-like factors {2.3.3.10} | ||||||||
| HGNC | HGNC:14097 | ||||||||
| EntrezGene | GeneID:64288 (SSTAR profile) | ||||||||
| UniProt ID | ZSC31_HUMAN | ||||||||
| UniProt AC | Q96LW9 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | ZSCAN31 expression | ||||||||
| ReMap ChIP-seq dataset list | ZSCAN31 datasets | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 6.0 | 5.0 | 42.0 | 35.0 | 8.0 | 14.0 | 15.0 | 3.0 | 15.0 | 20.0 | 46.0 | 4.0 | 3.0 | 10.0 | 13.0 | 5.0 |
| 02 | 7.0 | 3.0 | 16.0 | 6.0 | 10.0 | 21.0 | 1.0 | 17.0 | 58.0 | 31.0 | 6.0 | 21.0 | 2.0 | 35.0 | 3.0 | 7.0 |
| 03 | 28.0 | 1.0 | 45.0 | 3.0 | 45.0 | 3.0 | 28.0 | 14.0 | 7.0 | 2.0 | 8.0 | 9.0 | 4.0 | 2.0 | 42.0 | 3.0 |
| 04 | 4.0 | 0.0 | 25.0 | 55.0 | 2.0 | 0.0 | 3.0 | 3.0 | 7.0 | 11.0 | 60.0 | 45.0 | 1.0 | 1.0 | 22.0 | 5.0 |
| 05 | 3.0 | 9.0 | 2.0 | 0.0 | 3.0 | 8.0 | 0.0 | 1.0 | 16.0 | 79.0 | 9.0 | 6.0 | 1.0 | 71.0 | 29.0 | 7.0 |
| 06 | 13.0 | 7.0 | 2.0 | 1.0 | 102.0 | 22.0 | 21.0 | 22.0 | 5.0 | 7.0 | 25.0 | 3.0 | 6.0 | 1.0 | 5.0 | 2.0 |
| 07 | 18.0 | 1.0 | 106.0 | 1.0 | 4.0 | 0.0 | 32.0 | 1.0 | 44.0 | 0.0 | 9.0 | 0.0 | 1.0 | 1.0 | 26.0 | 0.0 |
| 08 | 58.0 | 8.0 | 1.0 | 0.0 | 0.0 | 1.0 | 0.0 | 1.0 | 2.0 | 165.0 | 1.0 | 5.0 | 0.0 | 2.0 | 0.0 | 0.0 |
| 09 | 0.0 | 0.0 | 2.0 | 58.0 | 120.0 | 4.0 | 35.0 | 17.0 | 1.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 6.0 | 0.0 |
| 10 | 1.0 | 0.0 | 120.0 | 0.0 | 0.0 | 0.0 | 4.0 | 0.0 | 1.0 | 2.0 | 40.0 | 0.0 | 0.0 | 0.0 | 76.0 | 0.0 |
| 11 | 0.0 | 0.0 | 2.0 | 0.0 | 1.0 | 0.0 | 1.0 | 0.0 | 15.0 | 1.0 | 214.0 | 10.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 12 | 1.0 | 0.0 | 15.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 76.0 | 0.0 | 139.0 | 2.0 | 3.0 | 0.0 | 7.0 | 0.0 |
| 13 | 42.0 | 37.0 | 2.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 4.0 | 156.0 | 1.0 | 0.0 | 0.0 | 2.0 | 0.0 | 0.0 |
| 14 | 10.0 | 3.0 | 0.0 | 33.0 | 111.0 | 21.0 | 18.0 | 45.0 | 0.0 | 1.0 | 2.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 15 | 29.0 | 15.0 | 66.0 | 11.0 | 5.0 | 2.0 | 13.0 | 5.0 | 11.0 | 3.0 | 4.0 | 2.0 | 1.0 | 27.0 | 44.0 | 6.0 |
| 16 | 1.0 | 0.0 | 8.0 | 37.0 | 6.0 | 6.0 | 27.0 | 8.0 | 7.0 | 10.0 | 54.0 | 56.0 | 1.0 | 3.0 | 10.0 | 10.0 |
| 17 | 1.0 | 4.0 | 7.0 | 3.0 | 6.0 | 7.0 | 4.0 | 2.0 | 67.0 | 11.0 | 19.0 | 2.0 | 10.0 | 5.0 | 9.0 | 87.0 |
| 18 | 72.0 | 2.0 | 8.0 | 2.0 | 8.0 | 4.0 | 9.0 | 6.0 | 11.0 | 14.0 | 12.0 | 2.0 | 81.0 | 4.0 | 5.0 | 4.0 |
| 19 | 8.0 | 13.0 | 17.0 | 134.0 | 1.0 | 5.0 | 11.0 | 7.0 | 2.0 | 12.0 | 16.0 | 4.0 | 0.0 | 2.0 | 7.0 | 5.0 |
| 20 | 0.0 | 0.0 | 10.0 | 1.0 | 10.0 | 7.0 | 13.0 | 2.0 | 8.0 | 11.0 | 26.0 | 6.0 | 43.0 | 6.0 | 95.0 | 6.0 |
| 21 | 7.0 | 33.0 | 15.0 | 6.0 | 7.0 | 8.0 | 4.0 | 5.0 | 19.0 | 31.0 | 88.0 | 6.0 | 1.0 | 5.0 | 6.0 | 3.0 |
| 22 | 7.0 | 4.0 | 11.0 | 12.0 | 16.0 | 39.0 | 7.0 | 15.0 | 72.0 | 16.0 | 14.0 | 11.0 | 2.0 | 1.0 | 7.0 | 10.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | -0.899 | -1.071 | 0.999 | 0.818 | -0.625 | -0.084 | -0.016 | -1.54 | -0.016 | 0.266 | 1.089 | -1.278 | -1.54 | -0.41 | -0.156 | -1.071 |
| 02 | -0.753 | -1.54 | 0.047 | -0.899 | -0.41 | 0.314 | -2.452 | 0.106 | 1.319 | 0.698 | -0.899 | 0.314 | -1.895 | 0.818 | -1.54 | -0.753 |
| 03 | 0.598 | -2.452 | 1.067 | -1.54 | 1.067 | -1.54 | 0.598 | -0.084 | -0.753 | -1.895 | -0.625 | -0.512 | -1.278 | -1.895 | 0.999 | -1.54 |
| 04 | -1.278 | -3.815 | 0.486 | 1.267 | -1.895 | -3.815 | -1.54 | -1.54 | -0.753 | -0.318 | 1.353 | 1.067 | -2.452 | -2.452 | 0.36 | -1.071 |
| 05 | -1.54 | -0.512 | -1.895 | -3.815 | -1.54 | -0.625 | -3.815 | -2.452 | 0.047 | 1.627 | -0.512 | -0.899 | -2.452 | 1.521 | 0.632 | -0.753 |
| 06 | -0.156 | -0.753 | -1.895 | -2.452 | 1.881 | 0.36 | 0.314 | 0.36 | -1.071 | -0.753 | 0.486 | -1.54 | -0.899 | -2.452 | -1.071 | -1.895 |
| 07 | 0.162 | -2.452 | 1.92 | -2.452 | -1.278 | -3.815 | 0.73 | -2.452 | 1.045 | -3.815 | -0.512 | -3.815 | -2.452 | -2.452 | 0.524 | -3.815 |
| 08 | 1.319 | -0.625 | -2.452 | -3.815 | -3.815 | -2.452 | -3.815 | -2.452 | -1.895 | 2.361 | -2.452 | -1.071 | -3.815 | -1.895 | -3.815 | -3.815 |
| 09 | -3.815 | -3.815 | -1.895 | 1.319 | 2.043 | -1.278 | 0.818 | 0.106 | -2.452 | -3.815 | -3.815 | -2.452 | -3.815 | -3.815 | -0.899 | -3.815 |
| 10 | -2.452 | -3.815 | 2.043 | -3.815 | -3.815 | -3.815 | -1.278 | -3.815 | -2.452 | -1.895 | 0.951 | -3.815 | -3.815 | -3.815 | 1.588 | -3.815 |
| 11 | -3.815 | -3.815 | -1.895 | -3.815 | -2.452 | -3.815 | -2.452 | -3.815 | -0.016 | -2.452 | 2.621 | -0.41 | -3.815 | -3.815 | -3.815 | -3.815 |
| 12 | -2.452 | -3.815 | -0.016 | -3.815 | -2.452 | -3.815 | -3.815 | -3.815 | 1.588 | -3.815 | 2.19 | -1.895 | -1.54 | -3.815 | -0.753 | -3.815 |
| 13 | 0.999 | 0.873 | -1.895 | -3.815 | -3.815 | -3.815 | -3.815 | -3.815 | -1.278 | 2.305 | -2.452 | -3.815 | -3.815 | -1.895 | -3.815 | -3.815 |
| 14 | -0.41 | -1.54 | -3.815 | 0.76 | 1.966 | 0.314 | 0.162 | 1.067 | -3.815 | -2.452 | -1.895 | -3.815 | -3.815 | -3.815 | -3.815 | -3.815 |
| 15 | 0.632 | -0.016 | 1.448 | -0.318 | -1.071 | -1.895 | -0.156 | -1.071 | -0.318 | -1.54 | -1.278 | -1.895 | -2.452 | 0.562 | 1.045 | -0.899 |
| 16 | -2.452 | -3.815 | -0.625 | 0.873 | -0.899 | -0.899 | 0.562 | -0.625 | -0.753 | -0.41 | 1.248 | 1.285 | -2.452 | -1.54 | -0.41 | -0.41 |
| 17 | -2.452 | -1.278 | -0.753 | -1.54 | -0.899 | -0.753 | -1.278 | -1.895 | 1.463 | -0.318 | 0.216 | -1.895 | -0.41 | -1.071 | -0.512 | 1.723 |
| 18 | 1.535 | -1.895 | -0.625 | -1.895 | -0.625 | -1.278 | -0.512 | -0.899 | -0.318 | -0.084 | -0.234 | -1.895 | 1.652 | -1.278 | -1.071 | -1.278 |
| 19 | -0.625 | -0.156 | 0.106 | 2.154 | -2.452 | -1.071 | -0.318 | -0.753 | -1.895 | -0.234 | 0.047 | -1.278 | -3.815 | -1.895 | -0.753 | -1.071 |
| 20 | -3.815 | -3.815 | -0.41 | -2.452 | -0.41 | -0.753 | -0.156 | -1.895 | -0.625 | -0.318 | 0.524 | -0.899 | 1.022 | -0.899 | 1.811 | -0.899 |
| 21 | -0.753 | 0.76 | -0.016 | -0.899 | -0.753 | -0.625 | -1.278 | -1.071 | 0.216 | 0.698 | 1.734 | -0.899 | -2.452 | -1.071 | -0.899 | -1.54 |
| 22 | -0.753 | -1.278 | -0.318 | -0.234 | 0.047 | 0.925 | -0.753 | -0.016 | 1.535 | 0.047 | -0.084 | -0.318 | -1.895 | -2.452 | -0.753 | -0.41 |