Model info
| Transcription factor | Thap11 | ||||||||
| Model | THA11_MOUSE.H11DI.0.B | ||||||||
| Model type | Dinucleotide PWM | ||||||||
| LOGO | 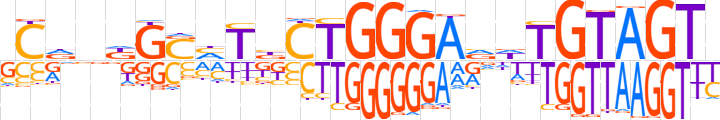 | ||||||||
| LOGO (reverse complement) | 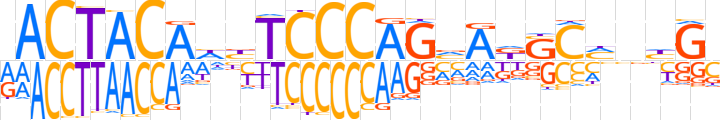 | ||||||||
| Data source | ChIP-Seq | ||||||||
| Model release | HOCOMOCOv11 | ||||||||
| Model length | 25 | ||||||||
| Quality | B | ||||||||
| Motif rank | 0 | ||||||||
| Consensus | SCdnKGSMTbCTGGGAvdTGTAGTY | ||||||||
| Best auROC (human) | 0.95 | ||||||||
| Best auROC (mouse) | 0.74 | ||||||||
| Peak sets in benchmark (human) | 2 | ||||||||
| Peak sets in benchmark (mouse) | 2 | ||||||||
| Aligned words | 107 | ||||||||
| TF family | THAP-related factors {2.9.1} | ||||||||
| TF subfamily | THAP11 (HRIHFB2206) {2.9.1.0.11} | ||||||||
| MGI | MGI:1930964 | ||||||||
| EntrezGene | GeneID:59016 (SSTAR profile) | ||||||||
| UniProt ID | THA11_MOUSE | ||||||||
| UniProt AC | Q9JJD0 (TFClass) | ||||||||
| Comment | |||||||||
| Downloads | pcm
pwm alignment threshold to P-value grid | ||||||||
| Standard thresholds |
| ||||||||
| GTEx tissue expression atlas | Thap11 expression | ||||||||
| Motifs in JASPAR |
PCM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | 0.0 | 8.0 | 0.0 | 0.0 | 1.0 | 24.0 | 4.0 | 3.0 | 0.0 | 57.0 | 0.0 | 3.0 | 0.0 | 5.0 | 0.0 | 2.0 |
| 02 | 1.0 | 0.0 | 0.0 | 0.0 | 38.0 | 5.0 | 41.0 | 10.0 | 2.0 | 2.0 | 0.0 | 0.0 | 1.0 | 1.0 | 6.0 | 0.0 |
| 03 | 7.0 | 8.0 | 19.0 | 8.0 | 2.0 | 2.0 | 1.0 | 3.0 | 10.0 | 17.0 | 14.0 | 6.0 | 3.0 | 3.0 | 2.0 | 2.0 |
| 04 | 2.0 | 2.0 | 12.0 | 6.0 | 6.0 | 0.0 | 13.0 | 11.0 | 4.0 | 1.0 | 23.0 | 8.0 | 3.0 | 0.0 | 8.0 | 8.0 |
| 05 | 1.0 | 1.0 | 12.0 | 1.0 | 0.0 | 0.0 | 3.0 | 0.0 | 2.0 | 2.0 | 45.0 | 7.0 | 0.0 | 0.0 | 33.0 | 0.0 |
| 06 | 0.0 | 3.0 | 0.0 | 0.0 | 0.0 | 2.0 | 1.0 | 0.0 | 7.0 | 73.0 | 9.0 | 4.0 | 0.0 | 3.0 | 3.0 | 2.0 |
| 07 | 4.0 | 1.0 | 1.0 | 1.0 | 41.0 | 31.0 | 1.0 | 8.0 | 2.0 | 8.0 | 0.0 | 3.0 | 3.0 | 1.0 | 1.0 | 1.0 |
| 08 | 0.0 | 10.0 | 0.0 | 40.0 | 0.0 | 4.0 | 1.0 | 36.0 | 0.0 | 0.0 | 0.0 | 3.0 | 0.0 | 4.0 | 1.0 | 8.0 |
| 09 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 5.0 | 8.0 | 5.0 | 0.0 | 0.0 | 1.0 | 1.0 | 3.0 | 17.0 | 36.0 | 31.0 |
| 10 | 1.0 | 1.0 | 0.0 | 1.0 | 0.0 | 20.0 | 0.0 | 2.0 | 2.0 | 41.0 | 1.0 | 1.0 | 1.0 | 33.0 | 2.0 | 1.0 |
| 11 | 0.0 | 2.0 | 0.0 | 2.0 | 1.0 | 12.0 | 0.0 | 82.0 | 0.0 | 1.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 5.0 |
| 12 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 15.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 90.0 | 1.0 |
| 13 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 105.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 |
| 14 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 5.0 | 0.0 | 100.0 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 15 | 5.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 92.0 | 1.0 | 4.0 | 4.0 | 1.0 | 0.0 | 0.0 | 0.0 |
| 16 | 40.0 | 8.0 | 44.0 | 6.0 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 1.0 | 1.0 | 1.0 | 3.0 | 0.0 | 0.0 | 1.0 |
| 17 | 20.0 | 5.0 | 5.0 | 14.0 | 1.0 | 0.0 | 0.0 | 9.0 | 8.0 | 4.0 | 4.0 | 29.0 | 1.0 | 0.0 | 2.0 | 5.0 |
| 18 | 0.0 | 3.0 | 0.0 | 27.0 | 0.0 | 1.0 | 0.0 | 8.0 | 0.0 | 3.0 | 0.0 | 8.0 | 1.0 | 5.0 | 2.0 | 49.0 |
| 19 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 0.0 | 12.0 | 0.0 | 0.0 | 0.0 | 2.0 | 0.0 | 0.0 | 0.0 | 92.0 | 0.0 |
| 20 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 5.0 | 101.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 21 | 1.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 5.0 | 0.0 | 0.0 | 0.0 | 97.0 | 0.0 | 4.0 | 0.0 |
| 22 | 0.0 | 0.0 | 103.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 4.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 23 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 1.0 | 105.0 | 0.0 | 0.0 | 0.0 | 0.0 |
| 24 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 0.0 | 1.0 | 0.0 | 0.0 | 1.0 | 0.0 | 5.0 | 42.0 | 2.0 | 56.0 |
PWM
| AA | AC | AG | AT | CA | CC | CG | CT | GA | GC | GG | GT | TA | TC | TG | TT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 01 | -3.174 | 0.172 | -3.174 | -3.174 | -1.687 | 1.247 | -0.486 | -0.751 | -3.174 | 2.105 | -3.174 | -0.751 | -3.174 | -0.277 | -3.174 | -1.114 |
| 02 | -1.687 | -3.174 | -3.174 | -3.174 | 1.702 | -0.277 | 1.778 | 0.388 | -1.114 | -1.114 | -3.174 | -3.174 | -1.687 | -1.687 | -0.104 | -3.174 |
| 03 | 0.044 | 0.172 | 1.017 | 0.172 | -1.114 | -1.114 | -1.687 | -0.751 | 0.388 | 0.907 | 0.717 | -0.104 | -0.751 | -0.751 | -1.114 | -1.114 |
| 04 | -1.114 | -1.114 | 0.566 | -0.104 | -0.104 | -3.174 | 0.644 | 0.481 | -0.486 | -1.687 | 1.205 | 0.172 | -0.751 | -3.174 | 0.172 | 0.172 |
| 05 | -1.687 | -1.687 | 0.566 | -1.687 | -3.174 | -3.174 | -0.751 | -3.174 | -1.114 | -1.114 | 1.87 | 0.044 | -3.174 | -3.174 | 1.562 | -3.174 |
| 06 | -3.174 | -0.751 | -3.174 | -3.174 | -3.174 | -1.114 | -1.687 | -3.174 | 0.044 | 2.351 | 0.286 | -0.486 | -3.174 | -0.751 | -0.751 | -1.114 |
| 07 | -0.486 | -1.687 | -1.687 | -1.687 | 1.778 | 1.5 | -1.687 | 0.172 | -1.114 | 0.172 | -3.174 | -0.751 | -0.751 | -1.687 | -1.687 | -1.687 |
| 08 | -3.174 | 0.388 | -3.174 | 1.753 | -3.174 | -0.486 | -1.687 | 1.649 | -3.174 | -3.174 | -3.174 | -0.751 | -3.174 | -0.486 | -1.687 | 0.172 |
| 09 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -0.277 | 0.172 | -0.277 | -3.174 | -3.174 | -1.687 | -1.687 | -0.751 | 0.907 | 1.649 | 1.5 |
| 10 | -1.687 | -1.687 | -3.174 | -1.687 | -3.174 | 1.067 | -3.174 | -1.114 | -1.114 | 1.778 | -1.687 | -1.687 | -1.687 | 1.562 | -1.114 | -1.687 |
| 11 | -3.174 | -1.114 | -3.174 | -1.114 | -1.687 | 0.566 | -3.174 | 2.467 | -3.174 | -1.687 | -3.174 | -1.114 | -3.174 | -3.174 | -3.174 | -0.277 |
| 12 | -3.174 | -3.174 | -1.687 | -3.174 | -3.174 | -3.174 | 0.784 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | 2.56 | -1.687 |
| 13 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -1.687 | -3.174 | 2.714 | -3.174 | -3.174 | -3.174 | -1.687 | -3.174 |
| 14 | -3.174 | -3.174 | -1.687 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -0.277 | -3.174 | 2.665 | -1.687 | -3.174 | -3.174 | -3.174 | -3.174 |
| 15 | -0.277 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | 2.582 | -1.687 | -0.486 | -0.486 | -1.687 | -3.174 | -3.174 | -3.174 |
| 16 | 1.753 | 0.172 | 1.848 | -0.104 | -3.174 | -1.687 | -3.174 | -3.174 | -1.687 | -1.687 | -1.687 | -1.687 | -0.751 | -3.174 | -3.174 | -1.687 |
| 17 | 1.067 | -0.277 | -0.277 | 0.717 | -1.687 | -3.174 | -3.174 | 0.286 | 0.172 | -0.486 | -0.486 | 1.434 | -1.687 | -3.174 | -1.114 | -0.277 |
| 18 | -3.174 | -0.751 | -3.174 | 1.364 | -3.174 | -1.687 | -3.174 | 0.172 | -3.174 | -0.751 | -3.174 | 0.172 | -1.687 | -0.277 | -1.114 | 1.955 |
| 19 | -3.174 | -3.174 | -1.687 | -3.174 | -3.174 | -3.174 | 0.566 | -3.174 | -3.174 | -3.174 | -1.114 | -3.174 | -3.174 | -3.174 | 2.582 | -3.174 |
| 20 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -1.687 | -3.174 | -0.277 | 2.675 | -3.174 | -3.174 | -3.174 | -3.174 |
| 21 | -1.687 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -0.277 | -3.174 | -3.174 | -3.174 | 2.635 | -3.174 | -0.486 | -3.174 |
| 22 | -3.174 | -3.174 | 2.695 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -0.486 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 |
| 23 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -1.687 | -1.687 | 2.714 | -3.174 | -3.174 | -3.174 | -3.174 |
| 24 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -3.174 | -1.687 | -3.174 | -3.174 | -1.687 | -3.174 | -0.277 | 1.802 | -1.114 | 2.088 |